EN RESUMEN. Los análisis de suero de individuos vacunados con una o dos dosis de vacunas de ARNm contra 10 variantes circulantes de SARS-CoV-2, muestran que P.1 y B.1.351 en particular exhiben una neutralización limitada por inmunidad humoral inducida por la vacuna. Se encontró que este escape estaba mediado en gran parte por mutaciones en el dominio de unión al receptor del pico de SARS-CoV-2.
A partir de aquí: Traducción literal al idioma español del artículo OFICIAL DOI (IDENTIFICADOR DE OBJETOS DIGITALES.
https://doi.org/10.1016/j.cell.2021.03.013
Wilfredo F. Garcia-Beltran, Evan C. Lam, Kerri St. Denis, Adam D. Nitido, ZeidyH. Garcia, Blake M. Hauser, Jared Feldman, Maia N. Pavlovic, David J. Gregory,Mark C. Poznansky, Alex Sigal, Aaron G. Schmidt, A. John Iafrate, Vivek Naranbhai,Alejandro B. Balazs
Para aparecer en: Célula
Fecha de recepción: 12 de febrero de 2020
Fecha de revisión: 26 de febrero de 2021
Fecha de aceptación: 8 de marzo de 2021
Cite este artículo como: García-Beltrán, WF, Lam, EC, St. Denis, K., Nitido, AD, García, ZH, Hauser, BM, Feldman, J., Pavlovic, MN, Gregory, DJ, Poznansky, MC, Sigal, A., Schmidt, AG, Iafrate, AJ, Naranbhai, V., Balazs, AB, Varias variantes del SARS-CoV-2 escapan a la neutralización por inmunidad humoral inducida por la vacuna, Cell (2021), DOI: https://doi.org/10.1016/j.cell.2021.03.013
Este es un archivo PDF de un artículo que ha sufrido mejoras después de su aceptación, como la adición de una portada y metadatos, y el formato para facilitar la lectura, pero aún no es la versión definitiva del registro. Esta versión se someterá a corrección de estilo adicional, composición tipográfica y revisión antes de que se publique en su forma final, pero proporcionamos esta versión para dar visibilidad temprana del artículo. Tenga en cuenta que, durante el proceso de producción, se pueden descubrir errores que podrían afectar el contenido, y todas las renuncias legales que se aplican a la revista pertenecen. © 2021 El (los) autor (es). Publicado por Elsevier Inc.
P2
P3
Múltiples variantes del SARS-CoV-2 escapan a la neutralización por inmunidad humoral inducida por la vacuna

1 Estos autores contribuyeron igualmente
2 Departamento de Patología, Hospital General de Massachusetts, Boston, MA, 02114, EE. UU.
3 Departamento de Patología, Hospital Brigham and Women’s, Boston, MA, 02115, EE. UU.
4 Instituto Ragon de MGH, MIT y Harvard, Cambridge, MA, 02139, EE. UU.
5 Centro de vacunas e inmunoterapia, Hospital General de Massachusetts, Boston, MA, 02129, EE. UU.
6 Enfermedades infecciosas pediátricas, Hospital General para Niños de Massachusetts, Boston, MA 02114, EE. UU.
7 Departamento de Medicina, Hospital General de Massachusetts, Boston , MA, 02114, EE. UU.
8 Instituto de Investigación en Salud de África, Durban, 4001, Sudáfrica
9 Escuela de Trabajo atory Medicine and Medical Sciences, University of KwaZulu-Natal, Durban, 4041 South Africa
10Max Planck Institute for Infection Biology, Berlin, 10117, Germany
11 Dana-Farber Cancer Institute, Boston, MA, 02215, USA
12Center for the AIDS Program of Research in Sudáfrica, Durban, 4001, Sudáfrica
- Contacto principal; correspondencia: abalazs@mgh.harvard.edu
RESUMEN
La vacunación provoca respuestas inmunitarias capaces de neutralizar de forma potente el SARS-CoV-2. Sin embargo, la vigilancia en curso ha revelado la aparición de variantes que albergan mutaciones en spike, el principal objetivo de los anticuerpos neutralizantes. Para comprender el impacto de estas variantes, evaluamos la potencia de neutralización de 99 individuos que recibieron una o dos dosis de las vacunas BNT162b2 o ARNm-1273 contra pseudovirus que representan 10 cepas circulantes de SARS-CoV-2 en todo el mundo. Cinco de los 10 pseudovirus que albergaban mutaciones en el dominio de unión al receptor, incluidos K417N / T, E484K y N501Y, eran muy resistentes a la neutralización. La neutralización cruzada de las variantes de B.1.351 fue comparable al SARS-CoV y al WIV1-CoV derivado de murciélago, lo que sugiere que un número relativamente pequeño de mutaciones puede mediar un escape potente de las respuestas a la vacuna. Si bien el impacto clínico de la resistencia a la neutralización sigue siendo incierto, estos resultados destacan la posibilidad de que las variantes escapen de la inmunidad humoral neutralizadora y enfatizan la necesidad de desarrollar intervenciones protectoras amplias contra la pandemia en evolución. PALABRAS CLAVE: COVID-19; SARS-CoV-2; pico; variantes; RBD; anticuerpos neutralizantes; escapar
P4
INTRODUCCIÓN
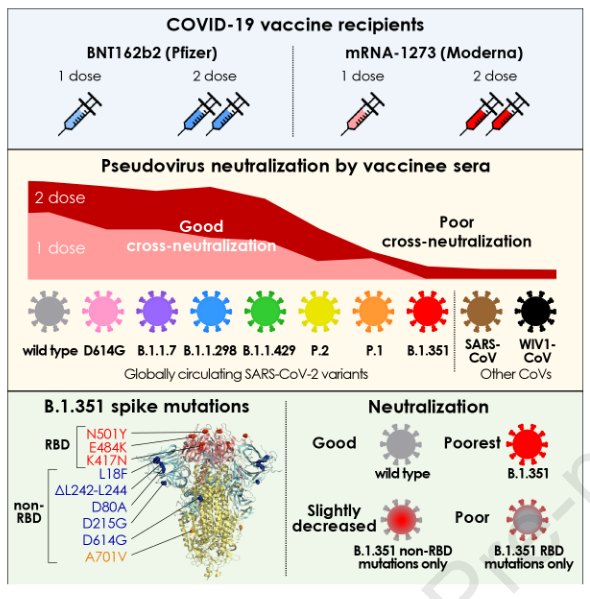
Desde la primera infección humana descrita con el síndrome respiratorio agudo severo coronavirus 2 (SARS-CoV-2) en diciembre de 2019, se han aprobado nueve vacunas para su uso en humanos (“COVID-19 Vaccine Tracker” n.d.). Dos de las vacunas que se utilizan actualmente en todo el mundo, BNT162b2 (fabricada por Pfizer) y mRNA-1273 (fabricada por Moderna), se basan en la liberación de nanopartículas lipídicas de mRNA que codifica una forma estabilizada de prefusión de proteína de pico derivada del SARS-CoV-2 aislado temprano en la epidemia de Wuhan, China. Ambas vacunas demostraron una eficacia> 94% en la prevención de la enfermedad por coronavirus 2019 (COVID-19) en estudios clínicos de fase III realizados a finales de 2020 en varios países (Polack et al. 2020; Baden et al. 2021). Sin embargo, la reciente aparición de nuevas variantes circulantes ha suscitado importantes preocupaciones sobre la eficacia geográfica y temporal de estas intervenciones. De hecho, los ensayos completados más recientemente de dos vacunas basadas en adenovirus (AZD1222 de Astrazeneca y JNJ-78436735 de Johnson & Johnson), una vacuna basada en nanopartículas (NVX-CoV2373 de Novavax) y una vacuna de proteína inactivada (Coronavac) han demostrado una reducción eficacia general («La vacuna Novavax COVID-19 demuestra una eficacia del 89,3% en el ensayo de fase 3 del Reino Unido» nd, «La vacuna AZD1222 alcanzó el criterio de valoración principal de eficacia en la prevención de COVID-19» 2020), y los análisis de subconjuntos sugieren una marcada variación geográfica con menor eficacia contra leves enfermedad a moderada en países como Sudáfrica y Brasil, donde la epidemia está dominada por cepas variantes. En conjunto, estos datos sugieren que las variantes resistentes a la neutralización pueden haber contribuido a estos resultados («Sudáfrica suspende el uso de la vacuna COVID-19 de AstraZeneca después de que no logra detener claramente la variante del virus» 2021; Herper et al. 2021). Una de las primeras variantes que surgió y rápidamente se convirtió en dominante a nivel mundial fue D614G. Si bien varios estudios demostraron que esta cepa es más infecciosa (Korber et al. 2020; Yurkovetskiy et al. 2020a, [b] 2020; Plante et al. 2020; Zhou et al. 2020; Hou et al. 2020), nosotros y otros encontraron que los sueros de individuos convalecientes mostraron una neutralización cruzada efectiva de las variantes de tipo salvaje y D614G (García-Beltran et al. 2021; Legros et al. 2021; Hou et al. 2020). Sin embargo, la vigilancia genómica reciente en el Reino Unido ha revelado una rápida expansión de un nuevo linaje denominado B.1.1.7 (también conocido como VOC-202012/01 o 501Y.V1). B.1.1.7 alberga 3 deleciones de aminoácidos y 7 mutaciones sin sentido en spike, que incluyen D614G y N501Y en el dominio de unión al receptor ACE2 (RBD), y se ha informado que es más infeccioso que D614G (Santos y Passos 2021; Galloway et al.2021; Liu et al.2021). Varios estudios han demostrado que los sueros de convalecientes y vacunados neutralizan de forma cruzada las variantes de B.1.1.7 con una potencia solo ligeramente disminuida, lo que sugiere que la infección previa o la vacunación con el SARS-CoV-2 de tipo salvaje aún pueden brindar protección contra las variantes de B.1.1.7
P5 y P6
(Wu et al. 2021; Muik et al. 2021; Shen et al. 2021; Rees-Spear et al. 2021; P. Wang et al. 2021). También ha habido informes de transmisión del SARS-CoV-2 entre humanos y visones en Dinamarca con una variante llamada grupo 5 de visón o B.1.1.298, que alberga una deleción de 2 aminoácidos y 4 mutaciones sin sentido, incluida Y453F en RBD. Las preocupaciones relacionadas con la transmisión entre especies en curso dieron como resultado el sacrificio de más de 17 millones de visones daneses para evitar una mayor propagación y evolución viral (Oude Munnink et al.2021; Oxner 2020). Otra variante que surgió recientemente en California, Estados Unidos, designada como B.1.429, contiene 4 mutaciones sin sentido en pico, una de las cuales es una única mutación L452R RBD. Aún no se ha determinado la capacidad de las variantes B.1.1.298 y B.1.429 para evadir la inmunidad humoral neutralizante de una infección o vacunación previa. De particular preocupación es una mutación E484K en RBD, que se identificó previamente a través de experimentos de selección in vitro para escapar de los anticuerpos monoclonales (Baum et al.2020) y también se identificó recientemente mediante un escaneo mutacional profundo como una variante con el potencial de evadir monoclonales y respuestas de anticuerpos en suero (Greaney et al. 2020, 2021). Las variantes novedosas que surgen del linaje B.1.1.28 descritas por primera vez en Brasil y Japón, denominadas P.2 (con mutaciones de sentido erróneo de 3 picos) y P.1 (con mutaciones de sentido erróneo de 12 picos), contienen esta mutación E484K y P.1 en particular también contiene mutaciones K417T y N501Y en RBD. Estas cepas se han propagado rápidamente, y tanto P.2 como P.1 se encontraron recientemente en casos documentados de reinfección por SARS-CoV-2 (Paiva et al. 2020; Faria et al. 2021; Resende et al. 2021; Naveca et al.2021; Nonaka et al.2021). La mayor preocupación ha sido la aparición de múltiples cepas del linaje B.1.351 (también conocido como 501Y.V2), que se informaron por primera vez en Sudáfrica y desde entonces se han extendido por todo el mundo (Tegally et al. 2021). Este linaje tiene tres mutaciones RBD, K417N, E484K y N501Y, además de varias mutaciones fuera de RBD, y varios informes han sugerido que los sueros de convalecientes y vacunados tienen una neutralización cruzada disminuida de variantes del linaje B.1.351 (P. Wang et al. 2021; Wibmer et al.2021; Wu et al.2021; Hu et al.2021). Una limitación clave de varios de estos informes ha sido el uso de mutaciones únicas o combinaciones de mutaciones que no ocurren naturalmente. Independientemente, la aparición de variantes novedosas que parecen escapar de las respuestas inmunes ha impulsado a los fabricantes de vacunas a desarrollar refuerzos para estas variantes de picos (“Moderna Developing Booster Shot for New Virus Variant B.1.351” n.d.). Aquí, evaluamos sistemáticamente el potencial de neutralización de los sueros de una cohorte de individuos que recibieron una o dos dosis de la vacuna BNT162b2 (Pfizer) o mRNA-1273 (Moderna) contra los pseudovirus del SARS-CoV-2 que portan proteínas de punta que se encuentran en las cepas circulantes. . Utilizamos nuestro ensayo de neutralización de pseudovirus de alto rendimiento descrito anteriormente (García-Beltran et al.2021) para cuantificar la neutralización contra variantes que surgen por primera vez en el Reino Unido (B.1.1.7), Dinamarca (B.1.1.298 ), Estados Unidos (B.1.429), Brasil y Japón (P.2 y P.1) y Sudáfrica (tres variantes del linaje B.1.351), así como el SARS-CoV del brote de 2002 en Hong Kong y el coronavirus de murciélago preemergente WIV1-CoV. Encontramos que, aunque la neutralización se conserva en gran medida contra muchas variantes, las que contienen las mutaciones K417N / T, E484K y N501Y RBD, es decir, las variantes P.1 y B.1.351, han disminuido significativamente la neutralización incluso en individuos completamente vacunados. Los individuos que recibieron solo una única dosis reciente de vacuna tuvieron títulos de neutralización más débiles en general y no mostraron neutralización detectable de variantes de B.1.351 en nuestros ensayos. Tomados en conjunto, nuestros resultados destacan que las vacunas BNT162b2 y mRNA-1273 logran solo una neutralización cruzada parcial de nuevas variantes y respaldan la reformulación de vacunas existentes para incluir diversas secuencias de picos. En última instancia, puede ser necesario el desarrollo de nuevas vacunas capaces de provocar anticuerpos ampliamente neutralizantes para resolver la pandemia en curso.
P7
RESULTADOS
Aparición y propagación mundial de variantes preocupantes del SARS-CoV-2
Desde el primer caso descrito de infección por SARS-CoV-2 en Wuhan, China, en diciembre de 2019, se han documentado más de 107 millones de infecciones confirmadas (Coronavirus.jhu.edu), lo que permite la diversificación viral y el surgimiento de seis linajes principales distintos con numerosos variantes. Un subconjunto de estas variantes ha sido denotado como variantes de preocupación por la Organización Mundial de la Salud dada la presencia de mutaciones con potencial para aumentar la transmisibilidad, virulencia o evadir las respuestas inmunes. Nos centramos en las variantes preocupantes descritas por primera vez en el Reino Unido (B.1.1.7), Dinamarca (B.1.1.298), Estados Unidos (B.1.429), Brasil y Japón (P.2 y P.1), y Sudáfrica (B.1.351), la mayoría de los cuales surgieron a fines de 2020 (Figura 1A-B). Aunque las mutaciones que surgen naturalmente en estas variantes abarcan toda la proteína de pico, ocurren principalmente en S1 y RBD, el principal objetivo de los anticuerpos neutralizantes (Figura 1C y S1). Después de analizar las secuencias de pico de SARS-CoV-2 depositadas para cada linaje en GISAID, identificamos mutaciones de secuencia de consenso que representan la cepa circulante dominante para cada linaje (Figura 1D y S1). En el caso del linaje B.1.351, estudiamos tres de las variantes dominantes que comprenden la mayoría de las secuencias depositadas, que designamos v1, v2 y v3. Las tres mutaciones principales de RBD de interés son: (i) N501Y, presente en las variantes B.1.1.7, P.1 y B.1.351; (ii) E484K, presente en las variantes P.2, P.1 y B.1.351; y (iii) K417T para la variante P.1 y K417N para las variantes B.1.351. Por separado, la variante B.1.1.298 encontrada en visones daneses contenía una mutación Y453F en RBD, y la variante B.1.429 de California contenía un L452R. Aunque son parientes lejanos, el SARS-CoV del brote de coronavirus de Hong Kong de 2002 y el WIV1-CoV preemergente derivado de murciélagos comparten una homología de pico de ~ 76% con el SARS-CoV-2 y se evaluaron para proporcionar una comparación con coronavirus serológicamente distintos (Figura 1A y 1D).
Respuestas de neutralización provocadas por la vacuna a las cepas circulantes de SARS-CoV-2
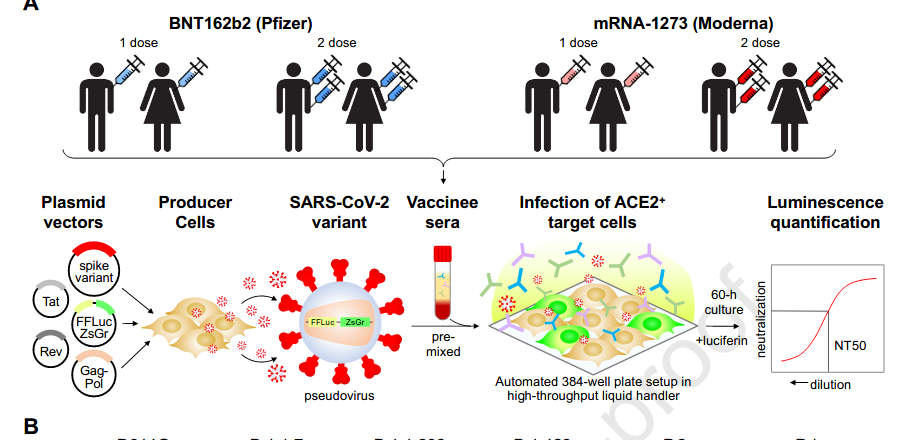
Acumulamos una cohorte de 99 individuos que recibieron una o dos dosis completas de las vacunas BNT162b2 o mRNA-1273, y usamos un ensayo de neutralización de pseudovirus lentivíricos basado en luminiscencia que nosotros y otros han validado previamente (C. Wang et al. 2020; Ju et al. 2020; Pinto et al. 2020; Yang et al. 2020; Moore et al. 2004; Crawford et al. 2020; García-Beltran et al. 2021 ) para evaluar la neutralización de las variantes del SARS-CoV-2 en un sistema de alto rendimiento (Figura 2A-B). Esta cohorte era relativamente joven (mediana de edad: 33 años, rango: 22 – 73 años) y el 62,6% (62/99) mujeres y el 37,4% (37/99) hombres (Figura S2). Comparamos sueros de 1220 muestras prepandémicas que habíamos analizado previamente utilizando el mismo ensayo (García-Beltrán et al. 2021) con nuestra cohorte de vacunados. El análisis de las características operativas del receptor mostró
P8
que el ensayo de neutralización de pseudovirus fue capaz de discriminar con precisión entre individuos no vacunados y vacunados ≥7 días después de la segunda dosis de BNT162b2 o mRNA-1273 (AUC = 0,9998), con una sensibilidad del 100% y una especificidad de 99% utilizando el límite de detección del ensayo (pNT50 de 12) como punto de corte (Figura S3). Entre los no vacunados y los individuos que recibieron 1 dosis de vacuna (o <7 días después de la segunda dosis), la sensibilidad se redujo al 93% (Figura S3). Los sueros obtenidos de individuos que recibieron 2 dosis completas de vacuna mostraron una fuerte neutralización del pseudovirus del SARS-CoV-2 de tipo salvaje, con los receptores de BNT162b2 logrando un título medio de 2.016 y los receptores de ARNm-1273 con un título medio de 762 (esta diferencia no fue estadísticamente significativo) (Figura 3A). Los individuos que recibieron solo una dosis de vacuna (o <7 días después de la segunda dosis) tuvieron una neutralización significativamente más baja, pero fácilmente detectable, con títulos medios de 167 para BNT162b2 y 208 para mRNA-1273 (Figura 3C). Al comparar el título de neutralización de pseudovirus en función del tiempo posterior a la vacunación, observamos un aumento esperado en el título después de la segunda dosis (Figura 3B). La magnitud de la neutralización se correlacionó con los niveles totales de anticuerpos anti-RBD; sin embargo, esta correlación fue pobre dado que la mayoría de los vacunados alcanzaron el límite superior de detección de nuestro ELISA (Figura 3C). Ni el sexo ni la edad parecieron influir significativamente en los títulos de neutralización en nuestra cohorte (Figura 3D-E). La neutralización del pseudovirus D614G fue similar a la del tipo salvaje en individuos que recibieron dos dosis de vacuna (disminución de 1.2 veces para ambas vacunas de 2 dosis) (Figura 4A-D y S4A), lo que contrasta con estudios previos en sueros convalecientes. que nosotros y otros llevamos a cabo demostrando una neutralización ligeramente aumentada de la variante D614G frente al tipo salvaje (García-Beltrán et al. 2021) después de una infección natural. El efecto fue más pronunciado en los individuos que recibieron una dosis de vacuna, algunos de los cuales tenían una neutralización indetectable de D614G a pesar de la neutralización detectable del SARS-CoV-2 de tipo salvaje (Figura 4A-B). Esta diferencia puede ser una consecuencia de la vacuna que codifica la secuencia de picos de tipo salvaje, mientras que muchos individuos convalecientes en estudios anteriores probablemente estaban infectados con la variante D614G del SARS-CoV-2, dado que ya se había convertido en la cepa dominante a nivel mundial en el verano de 2020. (Lemieux et al. 2020; Korber et al. 2020). Al evaluar variantes que contienen una mutación RBD como parte de su paisaje mutacional, la variante B.1.1.7 (N501Y) del Reino Unido, la variante B.1.1.298 (Y453F) del visón danés y la variante B.1.429 (L452R) de California exhibieron una neutralización que fue generalmente similar a la de tipo salvaje y la variante D614G parental. Entre las personas que recibieron 2 dosis completas de
P9
BNT162b2, la disminución media de veces en la neutralización con respecto al tipo salvaje fue 2,1 veces para B.1.1.7, 1,4 veces para B.1.1.298 y 2,0 veces para B.1.429 (Figura 4C y S4A); para aquellos que recibieron 2 dosis completas de ARNm-1273, la disminución media de la neutralización en relación con el tipo salvaje fue de 2,3 veces para B.1.1.7, 1,3 veces para B.1.1.298 y 2,0 veces para B. 1.429 (Figura 4D y S4A). Sin embargo, la neutralización de la variante brasileña / japonesa P.2, cuyo RBD contiene una mutación E484K, se redujo significativamente (5,8 veces para BNT162b2, p <0,001; 2,9 veces para mRNA-1273, p <0,01) (Figura 4C- D y S4A). Esto está en línea con estudios previos que sugieren que la mutación E484K puede evadir respuestas de anticuerpos policlonales (Greaney et al. 2020; Jangra et al. 2021) y se ha encontrado en casos de reinfección por SARS-CoV-2 (Paiva et al. 2020). ; Faria et al.2021; Resende et al.2021; Naveca et al.2021; Nonaka et al.2021). De manera similar, las respuestas de anticuerpos neutralizantes también disminuyeron significativamente para la cepa P.1 brasileña / japonesa (6,7 veces para BNT162b2, p <0,0001; 4,5 veces para mRNA-1273, p <0,001), que alberga tres mutaciones en RBD (K417T , E484K y N501Y) y también se ha encontrado en casos de reinfección (nuno_faria 2021). Sorprendentemente, la neutralización de las tres cepas sudafricanas B.1.351 se redujo sustancialmente para ambas vacunas de 2 dosis (v1: 34,5 veces para BNT162b2 y 27,7 veces para mRNA-1273; v2: 41,2 veces para BNT162b2 y 20,8 veces para ARNm-1273; v3: 42,4 veces para BNT162b2 y 19,2 veces para ARNm-1273; p <0,0001 para todas las comparaciones) (Figura 4C-D y S4A). Estas cepas contienen las mismas tres mutaciones RBD que P.1 excepto por una sustitución de asparagina frente a treonina en K417 (K417N) y varias mutaciones adicionales en regiones no RBD. Sorprendentemente, encontramos que la disminución en la neutralización de las cepas B.1.351 fue similar a la de los coronavirus relacionados lejanamente, a saber, SARS-CoV (43,8 veces para BNT162b2 y 33,5 veces para mRNA-1273) y WIV1-CoV (44,3- veces para BNT162b2 y 26,5 veces para ARNm-1273), lo que sugiere que un número relativamente pequeño de mutaciones puede medicar un escape potente de las respuestas de anticuerpos neutralizantes inducidas por la vacuna. Estas diferencias sustanciales en la neutralización no pudieron explicarse por diferencias en la expresión de la proteína de pico (Figura S4B) ni en la cantidad de pseudovirus usado en el ensayo (Figura S4C). En particular, el 36,7% (11/30) de los receptores de 2 dosis de BNT162b2 y el 42,9% (15/35) de los receptores de 2 dosis de las vacunas de mRNA-1273 no tuvieron neutralización detectable de al menos una de las variantes B.1.351 (Figura 4A -B). De los individuos que recibieron solo 1 dosis de BNT162b2 o mRNA-1273, todos tuvieron una neutralización indetectable de B.1.351 v2 y v3, excepto cuatro individuos que informaron haber tenido una infección previa por COVID-19 o una exposición significativa y un individuo para el cual no se obtuvo un historial de COVID-19. Esto sugiere que una sola dosis de vacunas de ARNm existentes puede ser insuficiente para inducir respuestas de anticuerpos neutralizantes cruzados en individuos no infectados previamente.
P10
Curiosamente, los seis individuos de nuestro estudio que informaron haber tenido una infección previa por COVID-19 o una exposición significativa tenían los títulos de neutralización más altos para la mayoría de las variantes y exhibieron una neutralización cruzada sustancial de B.1.351, SARS-CoV y WIV1-CoV (Figura 4A-B y S2). Esto sugiere que la infección previa combinada con la vacunación puede resultar en la mayor amplitud de respuestas de anticuerpos neutralizantes con reactividad cruzada, incluso contra coronavirus relacionados lejanamente.
La resistencia a la neutralización de las variantes de B.1.351 se debe principalmente a mutaciones de RBD.
Para caracterizar mejor el contexto mutacional responsable de la resistencia a la neutralización de B.1.351, exploramos la contribución de las mutaciones ubicadas tanto dentro como fuera de la región de pico de RBD. Es de destacar que muchas de las sustituciones y deleciones encontradas en el linaje B.1.351 están en estrecha proximidad estructural en el dominio S1 (Figura 5A). Sin embargo, el 86,2% de las secuencias de GISAID disponibles de este linaje albergan estas mutaciones en tres patrones distintos representados por B.1.351 v1 (46,6%), v2 (31,6%) y v3 (8,0%). Creamos pseudovirus en los que las regiones RBD de B.1.351 v1, v2 y v3 se revertieron a su secuencia original de Wuhan de tipo salvaje (v1 / wtRBD, v2 / wtRBD y v3 / wtRBD) mientras conservaban todos los demás B.1.351 v1 , v2 o v3 mutaciones. Sorprendentemente, los ensayos de neutralización realizados con sueros de 24 individuos que recibieron la vacuna BNT162b2 de 2 dosis revelaron que la neutralización de B.1.351 v1, v2 y v3 en ausencia de mutaciones RBD era comparable a la de D614G (Figura 5B-C). Un pseudovirus que lleva solo las tres mutaciones RBD (K417N, E484K y N501Y), en gran parte, pero no del todo, recapituló el fenotipo de escape (Figura 5B y 5D). A pesar de este escape, los anticuerpos mostraron unión reducida, pero detectable, a la proteína RBD mutante que alberga mutaciones B.1.351 (K417N, E484K y N501Y) por ELISA, que se correlacionó con la neutralización de pseudovirus K417N + E484K + N501Y (R2 = 0,67, p <0,0001 ) (Figura 5E). Esto sugiere que los anticuerpos provocados por la vacuna capaces de unirse al RBD mutante pueden conservar la capacidad de neutralizar los pseudovirus mutantes del RBD. Al evaluar la contribución de las mutaciones RBD frente a las no RBD hacia el escape, los análisis de regresión proporcionaron evidencia estadística de la interacción entre mutaciones dentro y fuera de RBD en la mediación del escape de variantes de B.1.351, consistente con los efectos sinérgicos (es decir, no aditivos) de estas mutaciones. (las estadísticas de interacción para B.1.351 v1 fue p = 0.06, v2 fue p <0.0001 y v3 fue p <0.0001). Estos resultados sugieren que, si bien las mutaciones RBD contribuyen con la mayor parte del escape observado de la neutralización inducida por la vacuna, son más efectivas cuando se encuentran en el contexto de mutaciones adicionales, particularmente las que se encuentran en las variantes B.1.351 v2 y v3.
P11
DISCUSIÓN
Tradicionalmente, se cree que las respuestas inmunes policlonales que surgen en el contexto de la infección y la vacunación se dirigen a múltiples epítopos antigénicos. Dada esta suposición, la expectativa sería que un pequeño número de variaciones en la secuencia de antígeno tuvieran solo efectos modestos sobre el reconocimiento por parte del sistema inmunológico. Aquí, encontramos que mientras muchas cepas, como B.1.1.7, B.1.1.298 o B.1.429, continúan siendo potentemente neutralizadas a pesar de la presencia de mutaciones individuales de RBD, otras variantes circulantes de SARS-CoV-2 escapan inmunidad humoral inducida por la vacuna. El P.2. La variante, que contiene una mutación E484K dentro de la región RBD, fue capaz de reducir significativamente la potencia de neutralización de individuos completamente vacunados, de acuerdo con lo sugerido por el escaneo mutacional profundo (Greaney et al. 2020; Jangra et al. 2021). De manera similar, la cepa P.1, que tiene tres mutaciones RBD, escapó de manera más efectiva a la neutralización, posiblemente explicando los casos recientemente reportados de reinfección con esta variante (Paiva et al.2020; Faria et al.2021; Resende et al.2021; Naveca et al.2021; Nonaka et al.2021). Finalmente, encontramos que las variantes de B.1.351 exhibieron una notable resistencia a la neutralización, en gran parte debido a tres mutaciones en RBD pero con una contribución medible de mutaciones no RBD. La magnitud del efecto es tal que las cepas B.1.351 escaparon a las respuestas de neutralización de la vacuna tan eficazmente como los coronavirus relacionados lejanamente. Dada la pérdida de la potencia de la vacuna contra varias variantes circulantes, la mayoría de los individuos que recibieron una sola dosis de vacuna no obtuvieron títulos de anticuerpos suficientes para proporcionar una neutralización cruzada detectable contra B.1.351 v2 o v3. Si bien nuestros estudios están limitados por el tiempo de seguimiento relativamente corto después de la vacunación, nuestros hallazgos respaldan la importancia de los regímenes de 2 dosis para lograr títulos, y quizás amplitud, para mejorar la protección contra variantes nuevas. Es importante considerar estos hallazgos en el contexto de las propuestas para administrar una dosis única de vacuna a un mayor número de personas en lugar de utilizar dosis para estimular a los receptores anteriores.Es importante destacar que nuestros estudios se basan en pseudovirus que solo son capaces de modelar la entrada dependiente de ACE2. paso del ciclo de vida del SARS-CoV-2. Si bien numerosos estudios ahora han demostrado una estrecha correlación entre los títulos de neutralización medidos contra pseudovirus y cultivos vivos de SARS-CoV-2 (C. Wang et al. 2020; Ju et al. 2020; Pinto et al. 2020; Yang et al. 2020; Moore et al.2004; Crawford et al.2020; Riepler et al.2020), no está claro qué impacto pueden tener mutaciones adicionales ubicadas fuera del pico en el escape inmunológico, la virulencia, la infectividad o la patogénesis. Varios informes y preimpresos recientes, incluidos los estudios realizados por Pfizer y Moderna, han producido hallazgos similares en términos de potencia de la vacuna contra las variantes B.1.1.7 y B.1.1.298, pero sustancialmente menos resistencia a la neutralización por
P12
B.1.351 de lo que medimos. Sin embargo, debemos advertir que cada estudio se realizó con distintas muestras de suero medidas utilizando diferentes condiciones (p. Ej., Virus de la estomatitis vesicular quimérica con capacidad de replicación versus pseudovirus lentiviral de entrada única) y con diferentes plásmidos de expresión de picos y combinaciones de mutaciones (p. Ej., Mutaciones triples RBD, mutaciones que definen el linaje, complemento completo de mutaciones que aún no se han observado juntas en la naturaleza, etc.). En el presente estudio, imitamos el patrón natural de mutaciones que se encuentran en las cepas circulantes, en fase. Es importante destacar que estos incluyen las variantes de picos que se encuentran en dos cepas de virus vivos competentes para la replicación del linaje B.1.351, que recientemente se informó que exhiben una resistencia a la neutralización casi completa en respuesta al plasma convaleciente (Cele et al. 2021). Las cepas utilizadas en el estudio mencionado anteriormente se designaron como 501Y.V2.HVdF002 y 501Y.V2.HV001, que tienen secuencias de proteínas de pico idénticas a las de los pseudovirus B.1.351 v1 y B.1.351 v2 informados en este estudio. Nuestro trabajo no aborda la inmunidad celular aportada por los linfocitos citotóxicos, incluidas las células T y NK. Incluso en ausencia de la inmunidad humoral neutralizante, estudios previos han sugerido que la inmunidad celular puede mitigar una infección grave o prolongada (Le Bert et al. 2020). En los individuos convalecientes, la inmunidad de las células T no se limitaría a los epítopos derivados de espigas, sino también a otras proteínas más abundantes como la nucleocápside. Como tal, sería razonable suponer que la inmunidad mediada por células T provocada por la infección permanecería en gran parte intacta para las variantes circulantes que incluyen B.1.351. De hecho, aunque los estudios recientes de Johnson & Johnson han demostrado una eficacia general reducida en Sudáfrica, hubo una protección sustancialmente mayor contra la enfermedad grave o fatal que contra la enfermedad leve a moderada (Herper et al. 2021). Sin embargo, con la excepción de las vacunas de virus enteros muertos, todos los diseños de vacunas disponibles actualmente solo proporcionan proteína de pico como inmunógeno diana, lo que limita la inmunidad de las células T a los epítopos de pico. No obstante, un estudio reciente ha demostrado que las mutaciones en los epítopos de las espigas no alteran las respuestas de las células T a pesar de escapar de los anticuerpos neutralizantes (Skelly et al. 2021). En resumen, nuestros datos destacan los desafíos que enfrentan todas las vacunas cuyos diseños se finalizaron temprano en la pandemia y se basaron en la secuencia del primer virus reportado en Wuhan, China. Dada la escala mundial y la magnitud de la pandemia en curso, incluidos los informes de casos de reinfección, está claro que la evolución viral continuará. Es posible que las vacunas actuales aún proporcionen un beneficio clínico contra variantes que exhiben una neutralización cruzada deficiente, como P.1 y B.1.351, al reducir la gravedad de la enfermedad COVID-19, pero esto aún no se ha determinado. En última instancia, será importante desarrollar intervenciones capaces de prevenir la transmisión de diversas variantes del SARS-CoV-2, incluidos los refuerzos de vacunas que se dirigen a estas
P13
variantes o tecnologías capaces de provocar o administrar anticuerpos ampliamente neutralizantes.
LIMITACIONES DEL ESTUDIO
El objetivo principal de este estudio fue evaluar el potencial de los sueros de los vacunados para neutralizar las variantes circulantes del SARS-CoV-2. Para ello, desarrollamos un ensayo de neutralización in vitro basado en pseudovirus lentivirales de alto rendimiento que utiliza una línea celular 293T-ACE2 diseñada como células diana. Como tal, estas células restringen la entrada de pseudovirus de una manera dependiente de ACE2 y carecen de otras proteínas de la superficie celular que pueden desempeñar un papel en la infección natural, como TMPRSS2 (Hoffmann et al. 2020) o NRP1 (Cantuti-Castelvetri et al. 2020). ). Se necesitan estudios adicionales para evaluar la influencia de estas proteínas en los títulos de neutralización sérica medidos. No evaluamos otras funciones mediadas por anticuerpos, como la deposición del complemento, la citotoxicidad celular dependiente de anticuerpos o la fagocitosis celular dependiente de anticuerpos, que pueden contribuir a la protección incluso en ausencia de anticuerpos neutralizantes. Además, no evaluamos el papel de las respuestas inmunitarias celulares provocadas por la vacuna mediadas por células T y células NK, que probablemente desempeñen un papel clave en la prevención de enfermedades para los receptores de la vacuna.
P14
AGRADECIMIENTOS, APOYO FINANCIERO
Queremos agradecer a Michael Farzan, PhD, por proporcionar células 293T que expresan ACE2. También agradecemos a Mandakolathur Murali, MD por muchas discusiones útiles y reveladoras. B.M.H. y cuenta con el respaldo del premio Número T32GM007753 del Instituto Nacional de Ciencias Médicas Generales. J.F. es compatible con T32AI007245. D.J.G., M.C.P. y M.N.P. fueron apoyados por el fondo de innovación VIC. COMO. fue apoyado por Bill y Melinda Gates Investment INV-018944 (AS) y por el South African Medical Research Council y el Departamento de Ciencia e Innovación (TdO), A.G.S. fue apoyado por NIH R01 AI146779 y una subvención del Consorcio de Massachusetts sobre Preparación para la Patogenia (MassCPR). A.J.I. cuenta con el apoyo de la Lambertus Family Foundation. TEJIDO. recibió el apoyo del Premio Avenir Nuevo Innovador DP2DA040254 de los Institutos Nacionales para el Abuso de Drogas (NIDA), el Programa de Académicos Transformadores de MGH, así como fondos de la Fundación Charles H. Hood. Esta investigación independiente fue apoyada por el Programa de Becarios de Investigación en Ciencias de Gilead en VIH.
CONTRIBUCIONES DEL AUTOR
W.F.G.B., E.C.L., K.S.D. y A.B.B. diseñó los experimentos. W.F.G.B., E.C.L., K.S.D., Z.G., A.D.N., V.N. y A.B.B. llevó a cabo experimentos y analizó datos. J.F., B.M.H. y A.G.S. proporcionó reactivos clave y discusiones e ideas útiles. D.J.G., M.C.P. y M.N.P. proporcionó muestras humanas para el estudio. A.D.N. y V.N. contribuido a los análisis estadísticos y de secuencia. A.J.I. y V.N. proporcionó discusiones clave y aportes al diseño experimental. W.F.G.B., V.N. y A.B.B. escribió el artículo con contribuciones de todos los autores.
DECLARACIONES DE INTERÉS
Los autores declaran no tener intereses en competencia
P15 a P20
Por favor referirse al artículo original en inglés. En estas páginas están explicadas la lista de figuras anexas al artículo así como los suplementos. Como son datos técnicos son perfectamente entendibles aún en inglés. https://doi.org/10.1016/j.cell.2021.03.013
P21
STAR ★ MÉTODOS
DISPONIBILIDAD DE RECURSOS.
Contacto principal. La información adicional y las solicitudes de recursos y reactivos deben ser dirigidas y serán atendidas por Alejandro Balazs (abalazs@mgh.harvard.edu).
Disponibilidad de materiales. Los plásmidos generados en este estudio estarán disponibles a través de Addgene. Las proteínas y anticuerpos recombinantes están disponibles en sus respectivas fuentes.
Disponibilidad de código y datos. Este estudio no generó código ni datos de secuencia. Los datos generados en el estudio actual (incluidos ELISA y neutralización) no se han depositado en un repositorio público, pero están disponibles del autor correspondiente a pedido.
MODELO EXPERIMENTAL Y DETALLES DEL SUJETO.
Sujetos humanos. El uso de muestras humanas fue aprobado por la Junta de Revisión Institucional de Partners (protocolo 2020P002274). Las muestras de suero de los receptores de la vacuna que recibieron una o dos dosis de la vacuna BNT162b2 o mRNA-1273 se recolectaron en tubos con tapa roja. Para cada individuo, se obtuvo información demográfica básica, incluida la edad y el sexo, así como cualquier historial relevante de COVID-19.
Líneas celulares. Se cultivaron células HEK 293T (ATCC) en DMEM (Corning) que contenía suero bovino fetal al 10% (VWR) y penicilina. / estreptomicina (Corning) a 37 ° C / CO2 al 5%. Las células 293T-ACE2 fueron un regalo de Michael Farzan (Scripps Florida) y Nir Hacohen (Broad Institute) y se cultivaron en las mismas condiciones. La confirmación de la expresión de ACE2 en células 293T-ACE2 se realizó mediante citometría de flujo.
DETALLES DEL MÉTODO.
Construcción de plásmidos de expresión de picos variantes. Para crear plásmidos de expresión de picos variantes, realizamos múltiples fragmentos de PCR
P22
utilizando oligonucleótidos que contienen cada mutación deseada (tecnología de ADN integrada) y utilizamos el ensamblaje de fragmentos superpuestos para generar el complemento completo de mutaciones para cada cepa. Es importante destacar que generamos estas mutaciones en el contexto de nuestro plásmido de expresión de pico de SARS-CoV-2 con codón optimizado previamente descrito que alberga una deleción de los 18 aminoácidos C-terminales que previamente demostramos que dan como resultado títulos de pseudovirus más altos. Los fragmentos ensamblados se insertaron en el vector pTwist-CMV-BetaGlobin-WPRE-Neo digerido con NotI / XbaI utilizando el kit de clonación In-Fusion HD (Takara). Todo el ADN plasmídico resultante utilizado en el estudio se verificó mediante secuenciación profunda de plásmido completo (Illumina) para confirmar la presencia de solo las mutaciones previstas.
Ensayo de neutralización de pseudovirus SARS-CoV-2. Para comparar la actividad neutralizante de los sueros vacunados contra los coronavirus, producimos partículas lentivirales pseudotipadas con diferentes proteínas de pico como se describió anteriormente (García-Beltrán et al. 2021). Brevemente, se produjeron pseudovirus en células 293T mediante transfección con PEI de un esqueleto lentiviral que codifica CMV-Luciferasa-IRES-ZsGreen así como plásmidos auxiliares lentivirales y cada plásmido de expresión de variante de pico. Después de la recolección y el filtrado, la producción se cuantificó titulando mediante citometría de flujo en células 293T-ACE2. Los ensayos de neutralización y la lectura se realizaron en un manipulador de líquidos Fluent Automated Workstation (Tecan) utilizando placas de 384 pocillos (Grenier). Se realizaron diluciones seriadas triples de 1:12 a 1: 8,748 para cada muestra de suero antes de agregar 50–250 unidades infecciosas de pseudovirus durante 1 h. Posteriormente, se añadieron a cada pocillo células 293T-ACE2 que contenían polibreno y se incubaron a 37ºC / CO2 al 5% durante 60-72 h. Después de la transducción, las células se lisaron usando un tampón que contenía luciferina (Siebring-van Olst et al. 2013) y se agitaron durante 5 min antes de la cuantificación de la expresión de luciferasa dentro de 1 h de la adición del tampón usando un luminómetro Spectramax L (Molecular Devices). El porcentaje de neutralización se determinó restando la luminiscencia de fondo medida en los pocillos de control celular (solo células) de los pocillos de muestra y dividiendo por los pocillos de control de virus (solo virus y células). Los datos se analizaron usando Graphpad Prism y los valores de pNT50 se calcularon tomando la inversa del valor de concentración inhibitoria del 50% para todas las muestras con un valor de neutralización de pseudovirus del 80% o más a la concentración más alta de suero.
Titulación de pseudovirus. Para determinar las unidades infecciosas de vectores lentivirales pseudotipados, se sembraron 400.000 células 293T-ACE2 por pocillo de una placa de 12 pocillos. 24 h más tarde, se hicieron tres diluciones seriadas de diez veces de sobrenadante puro de pseudovirus en 100 μL, que luego se utilizaron para reemplazar 100 μL de
P23
medio en las células en placa. Las células se incubaron durante 48 ha 37ºC / 5% de CO2 para permitir la expresión del gen indicador ZsGreen y se recolectaron con tripsina-EDTA (Corning). Las células se resuspendieron en PBS suplementado con FBS al 2% (PBS +) y se analizaron en un citómetro de flujo Stratedigm S1300Exi para determinar el porcentaje de células que expresan ZsGreen. Las unidades infecciosas se calcularon determinando el porcentaje de células infectadas en los pocillos que presentaban disminuciones lineales en la transducción y multiplicando por el número medio de células por pocillo determinado al inicio del ensayo. A MOI baja, se supuso que cada célula ZsGreen transducida representaba una única unidad infecciosa.
Evaluación citométrica de flujo de la expresión del pico. Para comparar la expresión superficial relativa de las proteínas variantes del pico de pseudovirus, se sembraron 400.000 células 293T por pocillo de una placa de 12 pocillos. 24 h más tarde, 1 μg de plásmido de expresión de pico variante y transfectado usando PEI. Las células se incubaron durante 48 ha 37 ° C y se recolectaron en PBS +. Las células transfectadas con cada vector se dividieron y se tiñeron con 5 μg / ml de S309, ADI-55689 o ADI-56046 durante 30 minutos a temperatura ambiente. Después, las células se lavaron con 1 ml de PBS +, se centrifugaron a 900 x gy se tiñeron con 2 µg / ml de anticuerpo policlonal anti-IgG-AF647 humana (Invitrogen) durante 30 minutos a temperatura ambiente. Las células se lavaron con 1 mL de PBS +, se centrifugaron a 900 x g, se resuspendieron en 100 μL de PBS +, se fijaron con 100 μL de PFA al 4% y se analizaron en un citómetro de flujo Stratedigm S1300Exi.
ELISA de anticuerpos totales del dominio de unión al receptor de SARS-CoV-2. La detección cuantitativa de anticuerpos totales al dominio de unión al receptor de SARS-CoV-2 (RBD) se realizó como se describió previamente (García-Beltran et al. 2021). Brevemente, utilizamos un ELISA indirecto con un estándar que consta de anticuerpo monoclonal anti-SARS-CoV y -CoV-2 (CR3022) (isotipo IgG1). Se recubrieron placas de ELISA de 96 pocillos con RBD de SARS-CoV-2 de tipo salvaje purificado. Las placas se bloquearon con BSA y se lavaron. Se creó una curva estándar de siete puntos utilizando CR3022-IgG1 a partir de 2 μg / ml realizando diluciones en serie 1: 3 con tampón de dilución, y las muestras de suero se diluyeron 1: 100 con tampón de dilución. Las muestras diluidas y los estándares se agregaron a los pocillos correspondientes y se incubaron durante 1 ha 37 ° C, seguido de lavado. Los anticuerpos totales se detectaron con anti-IgG humana + IgA + IgM (H + L) -HRP (Betil) diluido 1: 25.000 para una incubación de 30 min a temperatura ambiente. Después del lavado, se añadió sustrato TMB (Inova) a cada pocillo y se incubó durante 5-15 min antes de detenerlo con H2SO4 1 M. La densidad óptica (O.D.) se midió a 450 nm con la resta del O.D. a 570 nm como longitud de onda de referencia en un lector de microplacas SpectraMax ABS. Los niveles de anticuerpos anti-RBD se calcularon interpolando
P24
sobre la curva estándar y corrigiendo la dilución de la muestra; una unidad por mL (U / mL) se definió como la reactividad equivalente observada por 1 μg / mL de CR3022. En los ensayos en los que se usó RBD mutado que albergaba mutaciones K417N, E484K y N501Y, se realizó exactamente el mismo protocolo ELISA después de confirmar que nuestro estándar (CR3022-IgG1) se unía al RBD mutante frente al de tipo salvaje de forma casi idéntica.
CUANTIFICACIÓN Y ANÁLISIS ESTADÍSTICO. Los datos y los análisis estadísticos se realizaron utilizando GraphPad Prism 9.0.1, JMP Pro 15.0.0 (SAS Institute) y R v4.0.2. Los datos de citometría de flujo se analizaron utilizando FlowJo 10.7.1. Se realizaron ANOVA multivariados no paramétricos en las cifras indicadas donde estaban presentes varias cohortes; todos los valores de p se ajustaron para múltiples comparaciones. La significancia estadística se definió como p <0.05. Las barras de error en todas las cifras representan una desviación estándar. Los análisis de interacción / regresión se realizaron utilizando el paquete lm en R, utilizando estimaciones de pNT50 (normalizadas a tipo salvaje) para cada suero de donante y permitiendo la interacción entre las estimaciones de neutralización para cada variante de RBD de tipo salvaje (v1 / wtRBD, v2 / wtRBD, o v3 / wtRBD) y la variante que contiene solo mutaciones K417N + E484K + N501Y para explicar la neutralización compuesta de B.1351 v1, v2 y v3.
P25 hasta P28
Son las referencias. Favor descargar el archivo original en inglés. https://doi.org/10.1016/j.cell.2021.03.013
P29
ASPECTOS DESTACADOS.
● Han surgido a nivel mundial numerosas variantes de SRAS-CoV-2 que albergan mutaciones en pico
● Las vacunas de ARNm provocan una potente actividad neutralizante contra pseudovirus homólogos
● La neutralización cruzada de cepas con mutaciones en el dominio de unión al receptor (RBD) es deficiente
● Tanto RBD como no RBD las mutaciones median el escape de la inmunidad humoral inducida por la vacuna.
EN RESUMEN. Los análisis de suero de individuos vacunados con una o dos dosis de vacunas de ARNm contra 10 variantes circulantes de SARS-CoV-2, muestran que P.1 y B.1.351 en particular exhiben una neutralización limitada por inmunidad humoral inducida por la vacuna. Se encontró que este escape estaba mediado en gran parte por mutaciones en el dominio de unión al receptor del pico de SARS-CoV-2.
P30 a la P34
Tablas, imágenes y gráficos que pueden descargarse directaemnte de la versión original en inglés.

3 comentarios